Como hemos visto, para un alineamiento múltiple se necesitan tres o más secuencias de ADN o proteínas en formato multi-fasta.
Hay dos posibilidades para recolectar estas secuencias:
1. A partir de una secuencia anónima:
MVKPIIAPSI LASDFANLGC ECHKVINAGA DWLHIDVMDG HFVPNITLGQ PIVTSLRRSV
PRPGDASNTE KKPTAFFDCH MMVENPEKWV DDFAKCGADQ FTFHYEATQD PLHLVKLIKS
KGIKAACAIK PGTSVDVLFE LAPHLDMALV MTVEPGFGGQ KFMEDMMPKV ETLRAKFPHL
NIQVDGGLGK ETIPKAAKAG ANVIVAGTSV FTAADPHDVI SFMKEEVSKE LRSRDLLD
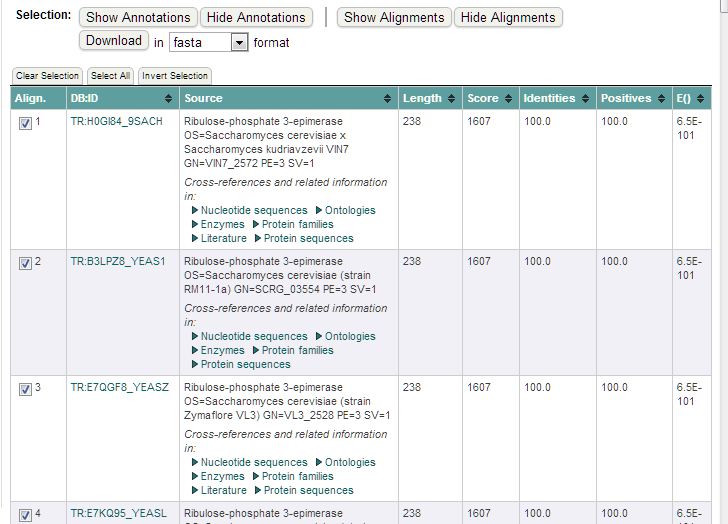
En este caso se usa FASTA para obtener las secuencias más relacionadas con esta secuencia problema. Marcaremos aquellas secuencias en las que estemos interesados:
Al pulsar sobre el boton ‘Download’ obtendremos nuestras secuencias en formato multi-fasta:
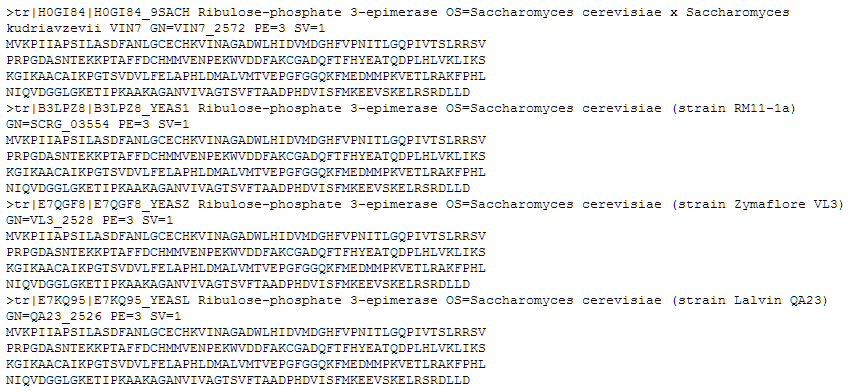
Copiando/pegando este multifasta en el Bloc de Notas, por ejemplo, podremos editar este archivo para poner el nombre adecuado a cada secuencia.