Usaremos el ejemplo clásico de Chu et al. (1998), The Transcriptional Program of Sporulation in Budding Yeast, Science, 282, 699-705 con los grupos de genes clusterizados de acuerdo con su perfil de expresión. Escogeremos un cluster de genes co-expresados y pondremos a prueba la hipótesis de que ‘los genes con función similar tienden a co-expresarse’.
Los archivos para este ejercicio son el cluster de genes coexpresados ‘sporulation_clu42.txt‘ y el resto de genes en el experimento ‘sporulation_all_but_clu42.txt‘ de Saccharomyces cerevisiae. Guarde ambos archivos en su máquina local y súbalos a Babelomics (Upload) escogiendo el tipo de datos ID list -> Id
Lance un nuevo trabajo Functional -> Single enrichment -> FatiGO:
- Elija la opción Id List vs. Id List
- Elija como List1 el grupo de genes co-expresados y como List2 el resto de genes del experimento
- En Options deje las opciones por defecto
- En Select an organism elija Saccharomyces cerevisiae
- En la sección de bases de datos marque GO – biological process y GO – Cellular Component
- Ponga un nombre al trabajo (por ejemplo, sporulationFatiGO)
- Envie el trabajo al servidor (Launch job)
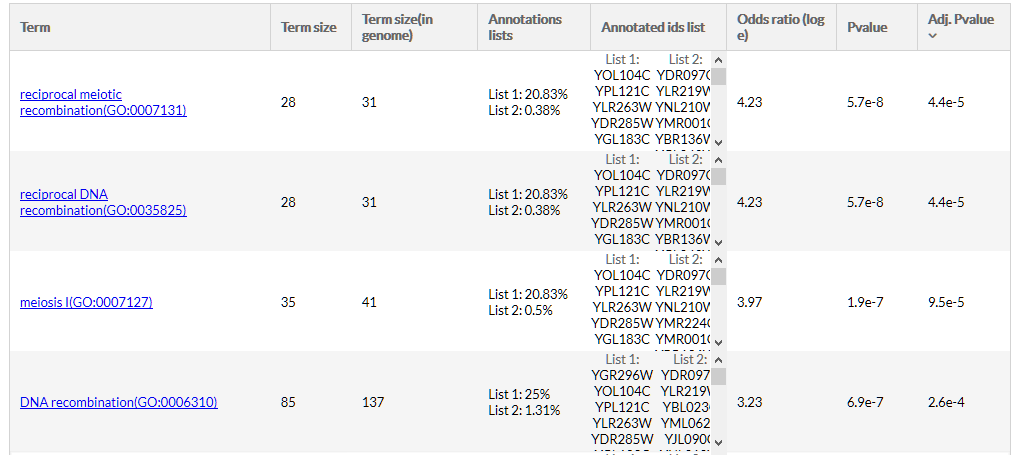
En la salida podremos ver que varios términos relacionados con la meiosis y con los cromosomas están significativamente sobre-representados en el cluster de genes co-expresados:
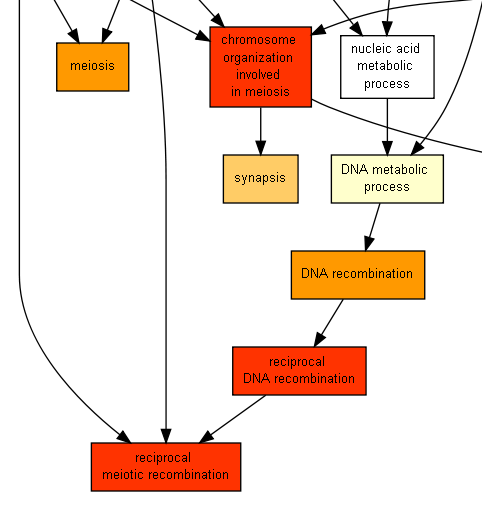
Network:
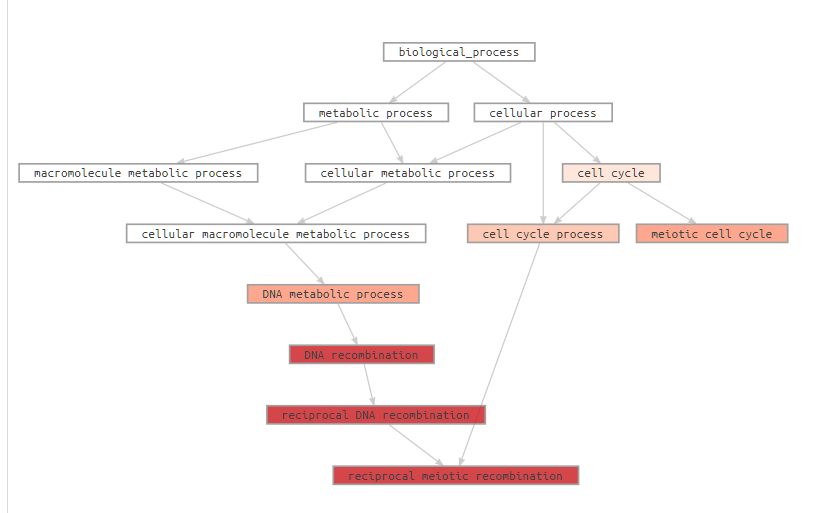
Repita el ejercicio con GOrilla y vea la salida gráfica (DAG):